DNA no Ensino de Biologia e Química
Felipe Vitório
Doutorando em Química (UFRRJ), professor da rede pública do Estado do Rio de Janeiro
O DNA (ácido desoxirribonucleico) é uma importante macromolécula orgânica que guarda todas as informações genéticas dos seres vivos (Moreira, 2003); é constituída pelas funções químicas: base nitrogenada, grupo fosfato e açúcar pentose que não possui em grupo hidroxila, dando o nome a este ácido nucleico. O ácido ribonucleico possui em sua pentose um grupo hidroxila e é comumente chamado por sua sigla RNA (Figura 1). O RNA é responsável pela síntese de proteínas da célula (Lehninger; Nelson; Cox, 2014).
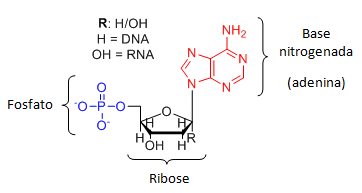
Figura 1: Estrutura do DNA/RNA.
O DNA é formado por unidades menores chamadas nucleotídeos, que são as bases nitrogenadas classificadas como purinas e pirimidinas. Existem cinco tipos diferentes de nucleotídeos, representados pelas letras A (Adenina), C (Citosina), G (Guanina), T (Timina); no RNA, no lugar na Timina, existe uma Uracila (U), todas representadas na Figura 2 (Solomons, 2013). Os arranjos desses nucleotídeos na estrutura do DNA é que faz com que os seres vivos sejam diferentes uns dos outros. Por isso, mínimas mutações causadas por fatores externos e internos ocorridas em apenas um nucleotídeo da uma das fitas de DNA podem alterar a produção de uma proteína importante e causar doenças genéticas (Berg; Stryer; Tymoczko, 2014).
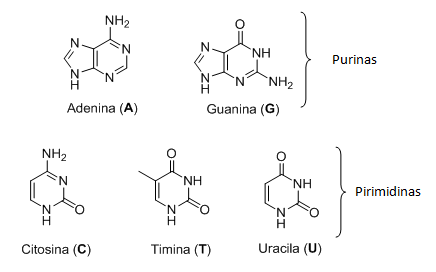
Figura 2: Estrutura das bases nitrogenadas presentes no DNA e RNA
Cada molécula de DNA é formada por duas fitas de nucleotídeos, que são ligados por interações de hidrogênio, o chamado DNA de dupla hélice. Esse modelo foi proposto pela primeira vez pelos cientistas norte-americanos James Watson (1928) e Francis Crick (1916), que mudaram a história da Biologia. O pareamento das bases nitrogenadas segue o seguinte padrão de combinação: A (adenina) sempre se liga com T (timina) e C (citosina) com G (guanina) (Watson; Crick, 1953).

Figura 3: Watson e Crick mostrando a primeira maquete da estrutura do DNA
O DNA está presente em todos os organismos vivos e geralmente está protegido no interior das células. As células apresentam uma camada lipídica, que é como uma camada de gordura, uma proteção para a célula (Lehninger; Nelson; Cox, 2014). Se quisermos isolar o DNA da célula, temos que romper a barreira lipídica; para isso podemos utilizar um detergente lava-louça para então extrair o DNA. Temos uma solução de meio intracelular, com a adição de sal grosso, para melhorar a visualização do DNA posteriormente, seguimos com uma filtração (pode ser utilizado um filtro de café).
A solução filtrada, enfim, é uma solução de DNA. Para poder vê-lo, na verdade ver um aglomerado de DNA, adicionamos etanol gelado, como sugerido no site O DNA vai à escola. Todos os materiais a serem utilizados e metodologias mais detalhadas estão disponíveis nesse site.
Esta prática propõe uma estratégia didática para um experimento de Química e Biologia em escolas de Ensino Médio e tem como objetivo entender e exemplificar o DNA isolado, associando conceitos de extração e filtração, interações intermoleculares e solubilidade. O procedimento é meramente ilustrativo, porque o DNA extraído está impuro.
Podemos abordar o DNA no ensino de Biologia, pois ele é encontrado nos estudos celulares (Wang; Sheng; Wen; Du, 2017), de mitocôndrias (Slusky, 2017), de clonagem (Yaghoubi; Aryan; Derakhshan; Meshkat, 2017) e de transgênicos (Herrera-Agudelo; Miró; Arruda, 2017), entre outros.
Na Química é abordado no estudo de suas interações de hidrogênio e as bases nitrogenadas (Suresh; Padhi; Pati; Priakumar, 2016), por exemplo. Quando quisermos unir as duas ciências, podem ser destacados os estudos de interação de micromoléculas com o DNA (Rahman; Choi; Choi; Yoo, 2017), compostos que são fluorescentes ao encontrar o DNA ou RNA, entre outros (Chen; Wei; Pan; Zhang; Dang; Zhang; Zhang, 2017).
Conhecer o DNA é fascinante; ter noção química e biológica de sua estrutura e funcionalidade é de extrema importância.
Referências
BERG, J. M.; STRYER, L; TYMOCZKO, J. L. Bioquímica. 7ª ed. Rio de Janeiro: Guanabara Koogan, 2014.
CHEN, H. Y.; WEI, J. R.; PAN, J. X.; ZHANG, W.; DANG, F. Q.; ZHANG, Z. Q.; ZHANG, J. Spectroscopic quantification of 5-hydroxymethylcytosine in genomic DNA using boric acid-functionalized nano-microsphere fluorescent probes. Biosensors and Bioelectronics, v. 91, p. 328-333, 2017.
HERRERA-AGUDELO, M.A.; MIRÓ, M.; ARRUDA, M.A.Z. In vitro oral bioaccessibility and total content of Cu, Fe, Mn and Zn from transgenic (through cp4 EPSPS gene) and nontransgenic precursor/successor soybean seeds. Food Chemistry, v. 225, p. 125-131, 2017.
LEHNINGER, A. L.; NELSON, D. L.; COX, M. M. Princípios de bioquímica de Lehninger. 6ª ed. Porto Alegre: Artmed, 2014.
MOREIRA, I. C. 50 anos da dupla hélice e as contribuições da Física. Física na Escola, v. 4, p. 5, 2003.
O DNA VAI À ESCOLA. Disponível em: http://www.odnavaiaescola.org.
RAHMAN, M. S.; CHOI, Y. H.; CHOI, Y. S.; YOO, J. C. Glycin-rich antimicrobial peptide YD1 from B. amyloliquefaciens, induced morphological alteration in and showed affinity for plasmid DNA of E. coli. AMB Express, v. 7, p. 8, 2017.
SLUSKY, J. S. Outer membrane protein design. Current Opinion in Structural Biology, v. 45, p. 45-52, 2017.
SOLOMONS, T. W. G. Química Orgânica. 9ª ed. São Paulo: LTC, 2013.
SURESH, G.; PADHI, S.; PATIL, I.; PRIYAKUMAR, U. D. Urea mimics nucleobases by preserving the helical integrity of B-DNA duplexes via hydrogen bonding and stacking interactions. Biochemistry, v. 55, p. 5.653-5.664, 2016.
WANG, L. J.; SHENG, M. Y.; WEN, P. C.; DU, J. Y. Morphological, physiological, cytological and phytochemical studies in diploid and colchicine-induced tetraploid plants of Fagopyrum tataricum (L.) Gaertn. Botanical Studies, v. 58, p. 1-12, 2017.
WATSON, J. D.; CRICK, F. H. C. Uma estrutura para o ácido desoxirribonucleico. Nature, v. 171, p. 737-738, 1953.
YAGHOUBI, A.; ARYAN, E.; DERAKHSHAN, M.; MESHKAT, Z. Design and construction of fusion genes hspX and tb10.4 from mycobacterium tuberculosis in a cloning vector. Koomesh, v. 19, p. 183-190, 2017.
Publicado em 22 de agosto de 2017
Novidades por e-mail
Para receber nossas atualizações semanais, basta você se inscrever em nosso mailing
Este artigo ainda não recebeu nenhum comentário
Deixe seu comentárioEste artigo e os seus comentários não refletem necessariamente a opinião da revista Educação Pública ou da Fundação Cecierj.

